 Protein sequence
Protein sequence | ID you entered: ENSP00000252669 Ensembl protein: ENSP00000252669  Protein sequence Protein sequence | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name: ACSBG2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Description: acyl-CoA synthetase bubblegum family member 2 [Source:HGNC Symbol;Acc:24174] | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Location: | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 chr19 p13.3 chr19 p13.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Gene Ontology: | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
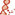 Biological process Biological process 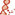 Molecular function Molecular function 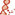 Cellular localization Cellular localization | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Interactions:  | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer_related variations : NA Interaction partner with cancer_related variations : NA | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer related differentially expressed proteins : NA Interaction partner with cancer related differentially expressed proteins : NA | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| NO. | csID | variation | change conservation+ | Domain | cancer name | PubMed | data source++ | validated dbSNP* | interface |
|---|---|---|---|---|---|---|---|---|---|
| 1 | cs25128 | R58Q | 1 | Skin Cancer | 21984974 | COSMIC | |||
| 2 | cs97419 | K310M | -1 | PF00501 | Breast Cancer | 21930502 21930507 | BIOMART | ||
| 3 | cs62949 | E481K | 1 | PF00501 | Head and Neck Cancer | 21984974 | COSMIC | ||
| 4 | cs83934 | G639D | -1 | Skin Cancer | 21984974 | COSMIC |
+Conservation of amino acid substitutions are defined here according to the BLOSUM62 matrix, conservative changes were those having a positive or neutral sign in the matrix, whereas non-conservative changes were those having a negative value (Cargill, et al. 1999). ++Data sources: HPI, COSMIC, OMIM, TCGA, BIOMART, Greenman2007, Sjoblom2006, Ding2008 *Cross-reference databases: dbSNP Interface information was collected from Wang 2012 |
| NO. | dbSNP_ID | variation | validated |
|---|---|---|---|
| 1 | rs76527006 | T7A | Cluster,1000Genome |
| 2 | rs79266675 | D13E | Cluster,Frequency,1000Genome |
| 3 | rs142290585 | R32* | Cluster,1000Genome |
| 4 | rs186319373 | I53T | 1000Genome |
| 5 | rs111748149 | L70H | Cluster |
| 6 | rs111748149 | L70P | Cluster |
| 7 | rs146288460 | N84S | 1000Genome |
| 8 | rs138620159 | R91W | Frequency |
| 9 | rs74980839 | S96Y | Cluster,Frequency,1000Genome |
| 10 | rs182356930 | R104C | 1000Genome |
| 11 | rs141138406 | L127I | Cluster,Frequency,1000Genome |
| 12 | rs4807840 | V143A | HapMap,1000Genome,Cluster,Frequency |
| 13 | rs33937754 | K152R | Cluster,Frequency,1000Genome |
| 14 | rs142462205 | Q165* | Frequency |
| 15 | rs74699889 | R205K | Cluster,Frequency,1000Genome |
| 16 | rs183816648 | I236L | 1000Genome |
| 17 | rs146465418 | I289T | 1000Genome |
| 18 | rs147009605 | Y365C | Frequency |
| 19 | rs147652076 | H392D | Cluster,Frequency,1000Genome |
| 20 | rs139677949 | A399V | Frequency |
| 21 | rs149994638 | F408L | Cluster,Frequency,1000Genome |
| 22 | rs143405303 | I461T | Frequency |
| 23 | rs181457077 | M544T | 1000Genome |
| 24 | rs149314396 | G568R | Frequency |
| 25 | rs35768768 | R583Q | Cluster,Frequency,1000Genome |
| 26 | rs17851959 | G584D | Cluster,Frequency,1000Genome |
| 27 | rs17851960 | G586D | Cluster,Frequency,1000Genome |
| 28 | rs145122124 | A589V | Frequency |
| 29 | rs35609668 | P601R | Cluster,Frequency,1000Genome |
| 30 | rs17856650 | R624K | Cluster,Frequency,1000Genome |
| 31 | rs17856651 | E626Q | Cluster,Frequency,1000Genome |
| 32 | rs35605352 | R650S | Cluster,Frequency |
No entry in dbDEPC was found |
| [ continue search ] |
Dr. Jing Li's Group
©2015 Menghuan Zhang, Jing Li

