 Protein sequence
Protein sequence | ID you entered: ENSP00000078445 Ensembl protein: ENSP00000078445  Protein sequence Protein sequence | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name: CREB3L3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Description: cAMP responsive element binding protein 3-like 3 [Source:HGNC Symbol;Acc:HGNC:18855] | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Location: | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 chr19 p13.3 chr19 p13.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Gene Ontology: | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
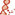 Biological process Biological process 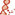 Molecular function Molecular function 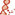 Cellular localization Cellular localization | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Interactions:  | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer_related variations : ( pvalue=0.0546396, hypergeometric test ) Interaction partner with cancer_related variations : ( pvalue=0.0546396, hypergeometric test ) 9 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer related differentially expressed proteins : NA Interaction partner with cancer related differentially expressed proteins : NA | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| NO. | csID | variation | change conservation+ | Domain | cancer name | PubMed | data source++ | validated dbSNP* | interface |
|---|---|---|---|---|---|---|---|---|---|
| 1 | cs90382 | T229P | -1 | Breast Cancer | 21930502 21930507 | BIOMART |
+Conservation of amino acid substitutions are defined here according to the BLOSUM62 matrix, conservative changes were those having a positive or neutral sign in the matrix, whereas non-conservative changes were those having a negative value (Cargill, et al. 1999). ++Data sources: HPI, COSMIC, OMIM, TCGA, BIOMART, Greenman2007, Sjoblom2006, Ding2008 *Cross-reference databases: dbSNP Interface information was collected from Wang 2012 |
| NO. | dbSNP_ID | variation | validated |
|---|---|---|---|
| 1 | rs149387566 | L26P | Frequency |
| 2 | rs201474344 | G35S | Cluster |
| 3 | rs143652660 | E44K | Cluster |
| 4 | rs77002741 | G105R | Cluster,Frequency,1000Genome |
| 5 | rs145839480 | G112S | Frequency |
| 6 | rs150887508 | H114P | Frequency |
| 7 | rs77528283 | P118A | Cluster,1000Genome |
| 8 | rs77528283 | P118T | Cluster,1000Genome |
| 9 | rs149917178 | G121E | Frequency |
| 10 | rs140312652 | D182N | Cluster,1000Genome |
| 11 | rs147422200 | S256L | 1000Genome |
| 12 | rs141474353 | Q312R | Cluster |
| 13 | rs150431015 | E380K | Frequency |
| 14 | rs145017010 | R392Q | Frequency |
| 15 | rs144785273 | A409T | Frequency |
| 16 | rs201461744 | R451C | Cluster |
No entry in dbDEPC was found |
| [ continue search ] |
Dr. Jing Li's Group
©2015 Menghuan Zhang, Jing Li

