 Protein sequence
Protein sequence | ID you entered: ENSP00000234347 Ensembl protein: ENSP00000234347  Protein sequence Protein sequence | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name: PRTN3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Description: proteinase 3 [Source:HGNC Symbol;Acc:HGNC:9495] | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Location: | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 chr19 p13.3 chr19 p13.3 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Gene Ontology: | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
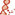 Biological process Biological process 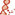 Molecular function Molecular function 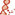 Cellular localization Cellular localization | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Interactions:  | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer_related variations : ( pvalue=0.263157, hypergeometric test ) Interaction partner with cancer_related variations : ( pvalue=0.263157, hypergeometric test ) 7 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer related differentially expressed proteins : ( pvalue=0.0328366, hypergeometric test ) Interaction partner with cancer related differentially expressed proteins : ( pvalue=0.0328366, hypergeometric test ) 5 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| NO. | csID | variation | change conservation+ | Domain | cancer name | PubMed | data source++ | validated dbSNP* | interface |
|---|---|---|---|---|---|---|---|---|---|
| 1 | cs35124 | Q78R | 1 | PF09342 PF00089 | Ovarian Cancer | 21720365 | COSMIC | SERPINB1 |
+Conservation of amino acid substitutions are defined here according to the BLOSUM62 matrix, conservative changes were those having a positive or neutral sign in the matrix, whereas non-conservative changes were those having a negative value (Cargill, et al. 1999). ++Data sources: HPI, COSMIC, OMIM, TCGA, BIOMART, Greenman2007, Sjoblom2006, Ding2008 *Cross-reference databases: dbSNP Interface information was collected from Wang 2012 |
| NO. | dbSNP_ID | variation | validated |
|---|---|---|---|
| 1 | rs140104242 | R4Q | Cluster,Frequency,1000Genome |
| 2 | rs351111 | V119I | Cluster,Frequency,1000Genome |
| 3 | rs144775105 | S125G | 1000Genome |
| 4 | rs113284122 | S131N | Cluster |
| 5 | rs150278723 | G149S | Frequency |
| 6 | rs145794662 | R159C | Cluster |
| 7 | rs139778046 | H185L | Cluster,Frequency,1000Genome |
| 8 | rs150802678 | R249H | Cluster,Frequency,1000Genome |
| NO. | dbDEPC_ID | change | ratio | cancer name | design | sample_control | sample_case | sample | pubmed |
|---|---|---|---|---|---|---|---|---|---|
| 1 | EXP00024 |  | Uterine Cancer | Normal vs. Cancer | Negative for Intraepithelial Lesions or Malignancy (NILM) | High-Grade Squamous Intraepithelial Lesion(HSIL) | tissue | 17902640 | |
| 2 | EXP00252 |  | Leukemia | Cancer vs. Cancer (subtype) | M1, M4, M5 acute myeloid leukemia subtypes | M2 and/or M3 acute myeloid leukemia subtypes | tissue | 15501966 |
| [ continue search ] |
Dr. Jing Li's Group
©2015 Menghuan Zhang, Jing Li

