 Protein sequence
Protein sequence | ID you entered: ENSP00000320493 Ensembl protein: ENSP00000320493  Protein sequence Protein sequence | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Name: TRIP10 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Description: thyroid hormone receptor interactor 10 [Source:HGNC Symbol;Acc:HGNC:12304] | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Location: | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 chr19 p13.3 chr19 p13.3 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Gene Ontology: | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
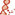 Biological process Biological process 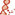 Molecular function Molecular function 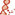 Cellular localization Cellular localization | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
Interactions:  | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer_related variations : ( pvalue=0.174169, hypergeometric test ) Interaction partner with cancer_related variations : ( pvalue=0.174169, hypergeometric test ) 17 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 Interaction partner with cancer related differentially expressed proteins : ( pvalue=0.0465225, hypergeometric test ) Interaction partner with cancer related differentially expressed proteins : ( pvalue=0.0465225, hypergeometric test ) 8 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| NO. | csID | variation | change conservation+ | Domain | cancer name | PubMed | data source++ | validated dbSNP* | interface |
|---|---|---|---|---|---|---|---|---|---|
| 1 | cs53986 | D260N | 1 | Ovarian Cancer | 18772890 21720365 | TCGA, COSMIC |
+Conservation of amino acid substitutions are defined here according to the BLOSUM62 matrix, conservative changes were those having a positive or neutral sign in the matrix, whereas non-conservative changes were those having a negative value (Cargill, et al. 1999). ++Data sources: HPI, COSMIC, OMIM, TCGA, BIOMART, Greenman2007, Sjoblom2006, Ding2008 *Cross-reference databases: dbSNP Interface information was collected from Wang 2012 |
| NO. | dbSNP_ID | variation | validated |
|---|---|---|---|
| 1 | rs142559634 | L89P | Frequency |
| 2 | rs140280835 | R97H | Cluster |
| 3 | rs140367724 | R122Q | Cluster |
| 4 | rs34329946 | Q133E | Cluster,Frequency |
| 5 | rs144960247 | R179Q | Cluster |
| 6 | rs137899128 | S180G | 1000Genome |
| 7 | rs192595827 | Y205C | 1000Genome |
| 8 | rs201404450 | F206C | Cluster |
| 9 | rs112745359 | S235* | Cluster |
| 10 | rs112745359 | S235L | Cluster |
| 11 | rs112745359 | S235W | Cluster |
| 12 | rs188886975 | N292S | 1000Genome |
| 13 | rs201134453 | R354H | Cluster,1000Genome |
| 14 | rs140822183 | S386G | Frequency |
| 15 | rs146733712 | L403F | Frequency |
| 16 | rs200262718 | R432Q | Cluster |
| 17 | rs28705365 | P436S | Cluster,Frequency,1000Genome |
| 18 | rs34808063 | A440T | Cluster,Frequency |
| 19 | rs144118150 | E459Q | Frequency |
| 20 | rs139253875 | E507K | Frequency |
No entry in dbDEPC was found |
| [ continue search ] |
Dr. Jing Li's Group
©2015 Menghuan Zhang, Jing Li

